伊藤 拓水
Teamセレブロンモジュレーターが分解誘導する新基質探索および基質認識モイエティの解析
研究分担者 伊藤 拓水東京医科大学医学総合研究所 客員准教授 |
研究概要
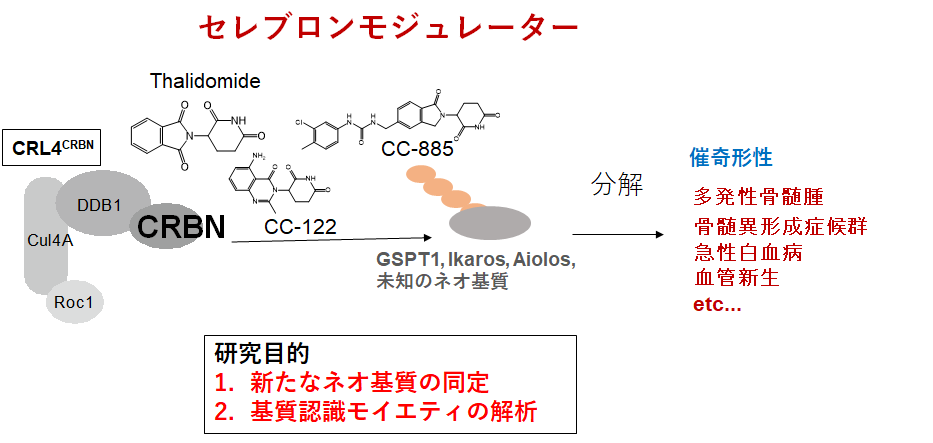
1950年代に開発されたサリドマイドは深刻な催奇性を有することで知られますが、現在においては抗がん作用など有用な作用を持つことがわかり再評価されています。我々が明らかにしましたサリドマイド標的因子セレブロン(CRBN)は現在ではリガンドの形状に応じて基質認識が変換されるユニークなユビキチンリガーゼCRL4CRBNとして機能することが判明しています(Ito et al. Science 2010)。現在、米国セルジーン社などによりサリドマイドを基にした新たな抗がん剤や抗炎症剤の開発が行われており、セレブロンに結合するこれら薬剤はセレブロンモジュレーターと呼ばれています。それらのうちレナリドミドやポマリドミドは既に臨床で認可されています。セレブロンモジュレーターの存在下でCRBNは新たな基質(ネオ基質)を分解誘導しますが、まだ未発見のネオ基質の多く、その全容は謎に包まれています。最近の我々の研究により、セレブロンモジュレーターにはセレブロン結合部分(グルタルイミド)と基質認識モイエティ(ベンゼン環含有)に分かれることが明らかになっていますが(Matyskiela et al. Nature 2016)、基質認識モイエティが具体的にどのようなルールに基づいて基質認識を変換させているかについては未だに不明です。本研究では新たなネオ基質探索・同定と基質認識モイエティの解析、また他の領域研究者とのコラボレーションにより新たなセレブロンモジュレーターの開発およびその分子機構についての理解を更に深めることを目的としています。
研究概要を示す模式図
本領域での研究成果
- Ando H, Sato T, Ito T, Yamamoto J, Sakamoto S, Nitta N, Asatsuma-Okumura T, Shimizu N, Mizushima R, Aoki I, Imai T, Yamaguchi Y, Berk AJ, Handa H.
Cereblon Control of Zebrafish Brain Size by Regulation of Neural Stem Cell Proliferation.
iScience 15, 95-108 (2019)
PMID: 31055217
プレスリリース - Asatsuma-Okumura T, Ando H, De Simone M, Yamamoto J, Sato T, Shimizu N, Asakawa K, Yamaguchi Y, Ito T, Guerrini L, Handa H.
p63 is a cereblon substrate involved in thalidomide teratogenicity.
Nat. Chem. Biol. 15, 1077-1084 (2019)
PMID: 31591562
プレスリリース - Tateno S, Iida M, Fujii S, Suwa T, Katayama M, Tokuyama H, Yamamoto J, Ito T, Sakamoto S, Handa H, Yamaguchi Y.
Genome-wide screening reveals a role for subcellular localization of CRBN in the anti-myeloma activity of pomalidomide.
Sci Rep. 10, 4012 (2020)
PMID: 32132601 - Yamamoto J, Suwa T, Murase Y, Tateno S, Mizutome H, Asatsuma-Okumura T, Shimizu N, Kishi T, Momose S, Kizaki M, Ito T, *Yamaguchi Y, *Handa H.
ARID2 is a pomalidomide-dependent CRL4CRBN substrate in multiple myeloma cells.
Nat. Chem. Biol. 16, 1208-1217 (2020)
PMID: 32958952 - Shimizu N, Asatuma-Okumura T, Yamamoto J, Yamaguchi Y, *Handa H,*Ito T.
PLZF and its fusion proteins are pomalidomide-dependent CRBN neosubstrates.
Commun Biol. 4, 1277 (2021)
PMID: 34764413
本領域での研究成果
- Ito T, Ando H, Suzuki T, Ogura T, Hotta K, Imamura Y, Yamaguchi Y, *Handa H.
Identification of a primary target of thalidomide teratogenicity.
Science 327, 1345-1350 (2010)
PMID: 20223979 - *Chamberlain P, Lopez-Girona A, Miller K, Carmel G, Pagarigan B, Chie-Leon B, Rychak E, Corral L, Ren Y, Wang M, Riley M, Delker S, Ito T, Ando H, Mori T, Hirano Y, Handa H, Hakoshima T, Daniel T, Cathers B.
Structure of the human cereblon-DDB1-lenalidomide complex reveals basis for responsiveness to thalidomide analogs.
Nat. Struct. Mol. Biol. 21, 803-809 (2014)
PMID: 25108355 - Matyskiela ME, *Lu G, Ito T (co-1st author), Pagarigan B, Lu C-C, Miller K, Fang W, Wang NY, Nguyen D, Houston J, Carmel G, Tran T, Riley M, Nosaka L, Lander GC, Gaidarova S, Xu S, Ruchelman AL, Handa H, Carmichael J, Daniel TO, Cathers BE, Lopez-Girona A, *Chamberlain PP.
A novel cereblon modulator recruits GSPT1 to the CRL4CRBN ubiquitin ligase.
Nature 535, 252-257 (2016)
PMID: 27338790 - Ito T, *Handa H.
Cereblon and its downstream substrates as molecular targets of immunomodulatory drugs.
Int. J. Hematol. 104, 293-299(2016)
PMID: 27460676 - Mori T, Ito T (co-1st author), Liu S, Ando H, Sakamoto S, Yamaguchi Y, Tokunaga E, Shibata N, *Handa H, *Hakoshima T.
Structural basis of thalidomide enantiomer binding to cereblon.
Sci. Rep. 8, 1294 (2018)
PMID: 29358579





